
错误信息
最近处理10x数据,需要把已有的亚群合并,然后绘制目标基因的热图~ 朴实~ 无华~ 枯燥~ 处理完成之后,需要调整亚群绘制顺序,基因的顺序 OK~ 我改~
one moment later……
“怎么这几张图的标度范围不一样?看起来不统一” 我改~ 也就是一个修改刻度~ 然后~ 然后我就后悔了~
漫漫Debug路
第一次尝试
Seurat包里面热图,用的是ggplot2绘制的,一般处理这种问题,只要
获取对象后重新指定一下数据标准化的范围就好,搞一下配色什么的就完
事
|
|
本以为这样就结束,打开结果一看?喵喵喵~ 什么鬼,那一条条的白线是个 什么玩意儿?
对比前后的结果,这些白色的部分在原始的图形中都被当作最大值处理(其 实是缺失值)。
没问题~ 缺失值替换为黄色就好
第二次处理
|
|
纳尼~ 那些组间的分隔怎么也变成了屎黄色?看来这样不对~
第三次处理
查看图形对象中那些缺失的数据数据(原本是会有一些细胞也为缺失的,但我更新之后的ggplot对象没法重复之前的结果,不记得之前ggplot2是哪个版本了)
|
|
这些奇怪名字的细胞就是用来生成那些组间分割的占位信息,在使用
na.value = "yellow" 时,把这些占位信息也给修改了,于是就有
了图中的屎黄色分割,处理方法也简单,只将那些正常细胞名称的表
达量由NA替换为我们的最大值即可~ 随后在scale_fill_gradientn中
将NA替换为白色即可~
第四次处理
本来经过前面的处理,应该已经可以正常将热图的标度修改为指定的 范围~ But~ 当我重新运行脚本时却出现了如下的报错:
|
|
我原来正常的脚本都跑不了了~这又是什么鬼~明明之前还好好的能够正常运行~
谷歌之~
Error in DoHeatmap – no labelling of identities above colourbar possible
看来是版本问题~
看一下自己环境里的r包,有人升级了ggplot2到3.3.3。
我也没有记录之前的ggplot2版本,之前的工作算是白做了~
看了一下Seurat的更新记录,最新的版本已经到了4.x.x,但所用对象使用的是3.1.1,所以找一个比较近的版本:
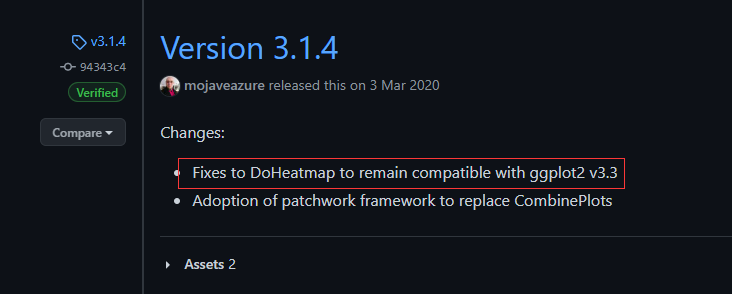 重新安装一个v3.1.4版本的Seurat
里面的
重新安装一个v3.1.4版本的Seurat
里面的DoHeatmap方法果然有所改变,对ggplot 3.3.3进行了适配
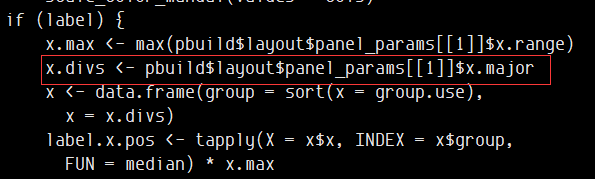
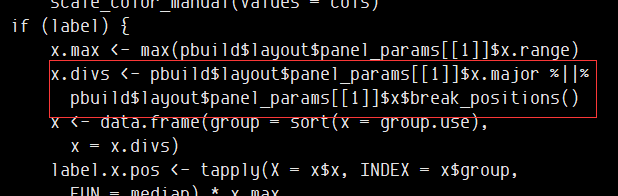 这个版本的ggplot2在重新标准化之后细胞不再会出现缺失值,前面的方法也呵呵了~
要消除白色的那些细胞,只需要将越过范围的值给赋值为其边界值即可
这个版本的ggplot2在重新标准化之后细胞不再会出现缺失值,前面的方法也呵呵了~
要消除白色的那些细胞,只需要将越过范围的值给赋值为其边界值即可
|
|
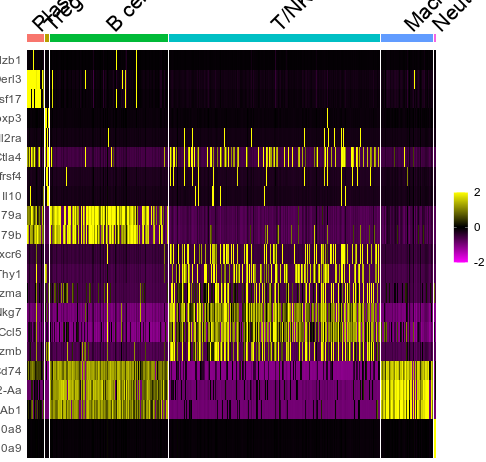 剩下的调整一下theme就好了
剩下的调整一下theme就好了